Estudiante
Departamento de Ingeniería Química y Bioquímica de la Universidad de Notre Dame.
Portada » Desarrollo de un pipeline para el análisis de imágenes de calcio

Estudiante
El calcio es un elemento que está presente en los procesos morfológicos de los tejidos de muchos organismos, tales como la división celular o el crecimiento. Actúa como un “segundo mensajero”, comunicando señales provenientes del medio y de otras células. Por esto, el desarrollo de moléculas fluorescentes que permiten visualizar cambios en las concentraciones de calcio al microscopio ha sido de gran utilidad para el estudio de estos fenómenos en el ámbito de la biología y la biotecnología. Esto ha hecho posible, por ejemplo, la representación de los cambios fisiológicos que se producen en un tejido en el tiempo.
Avances recientes en microscopía han permitido estudiar la dinámica del calcio con gran detalle, lo que ha entregado información muy valiosa acerca de lo que sucede en la célula en respuesta a distintos estímulos y cambios en su entorno. La gran cantidad de datos generados a partir de las imágenes de calcio han impulsado también el desarrollo de tecnologías que permiten extraer y analizar grandes volúmenes de información para luego interpretar su sentido biológico.
En el marco del programa The Bridge, el estudiante de pregrado Gabriel Miranda, bajo la guía del profesor Jeremiah Zartman, desarrolló un “pipeline” para el análisis de imágenes de calcio, utilizando diferentes softwares para extraer la información que describe el comportamiento del tejido, de manera cuantitativa, precisa y altamente automatizada.
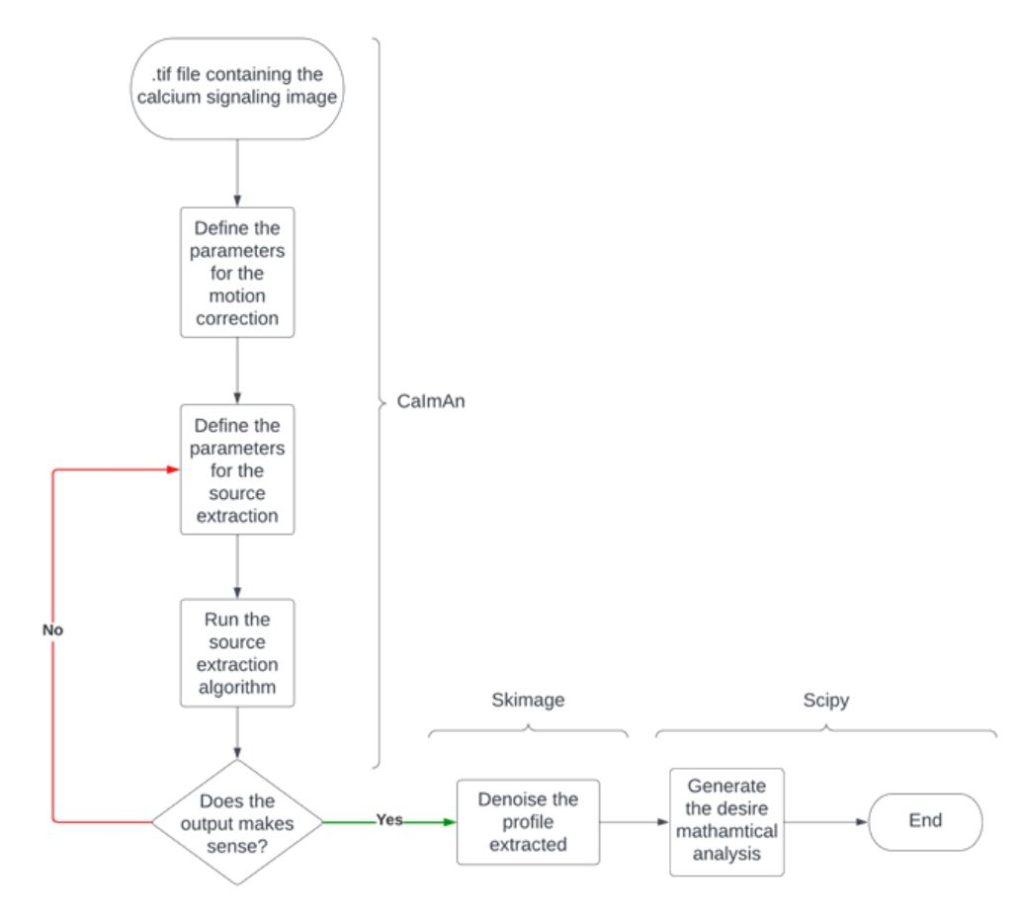
Fig. Flujo de trabajo del pipeline
Como primer paso del análisis consideraron la corrección de movimiento de las imágenes a través de algoritmos. Luego, guardaron las imágenes corregidas en un mapa de memoria para utilizarlas en la siguiente etapa de extracción de fuentes (source extraction), donde se detectaron las regiones de interés. Posteriormente, desarrollaron un análisis matemático para extraer características específicas de las señales de calcio, tales como su frecuencia de oscilación, el número total, la altura y el ancho de los peaks producidos durante la observación experimental.
Luego de concluir el diseño del pipeline, lo utilizaron para analizar los experimentos realizados en el laboratorio del profesor Zartman con moscas de la fruta (Drosophila melanogaster). En este modelo experimental se estudió la función del canal Piezo, una proteína de membrana que detecta estímulos mecánicos sobre las células durante procesos de división y muerte celular, asociados al desarrollo y la formación de distintos órganos. Estas señales se transmiten al formar un canal por el cual entran iones calcio a la célula, lo cual se traduce en efectos biológicos a nivel molecular que regulan estos procesos. Gracias a un compuesto químico llamado Yoda1, que puede activar artificialmente el canal Piezo, fue posible estudiar en detalle cómo afecta este canal el desarrollo del disco del ala de las moscas y la dinámica del calcio asociada. De esta forma demostraron que las señales de calcio transmitidas a través de Piezo son necesarias para controlar con precisión el tamaño de este órgano durante el desarrollo de las larvas de mosca, lo cual permite comprender mejor la función de esta proteína durante el desarrollo embrionario.
Gracias a la investigación realizada por Gabriel y el equipo del profesor Zartman, hoy es posible analizar las imágenes de calcio y extraer datos cuantitativos de manera automatizada, lo cual facilita la visualización, interpretación y comunicación de los resultados obtenidos en experimentos donde se estudia la dinámica de las señales de calcio en células y tejidos. En este caso, en particular, permitió saber qué estaba sucediendo durante el desarrollo del tejido del ala de las moscas al manipular experimentalmente la función del canal Piezo. El código asociado a este pipeline de análisis de imágenes, también permitirá a los investigadores que estudian señales de calcio en otros contextos implementar análisis de datos complejos sin necesidad de ser expertos en programación o ciencias de la computación.
Estudiante
Departamento de Ingeniería Química y Bioquímica de la Universidad de Notre Dame.

Estudiante